请问各位老师,如何合并两个图谱:Schafer_100和Melbourne subcortex atlas S2,并且转换为3mm分辨率呢?感谢!
- 这两个分区都提供了MNI空间的nii格式的文件,可以参考以前的帖子。
- 合并以后再重采样到3mm即可。
- 如果有没有说清楚的地方,再交流。
感谢回复!我按照以前的贴子运行了以下代码:
fslmaths Tian_Subcortex_S2_3T_1mm.nii.gz -add 100 -mas Tian_Subcortex_S2_3T_1mm.nii.gz MSA_reindex.nii.gz
fslmaths MSA_reindex.nii.gz -add schaefer100MNI_1mm.nii.gz combined_atlas.nii.gz
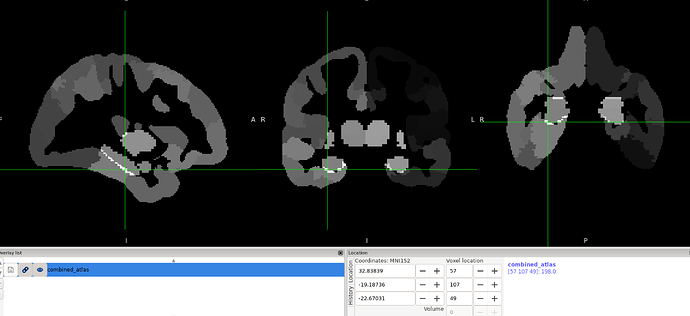
但是得到的combined_atlas.nii.gz,用fslstats -R指令查看强度范围是0~199,而不是预计的0~132。查看combined_atlas.nii.gz图像看,发现脑组织中有一些高强度的点。请问这个是什么原因呢?因为我之后想用合并后的图谱做功能连接分析,这个是不是会有影响呢?
- 应该是这两个分区模板之间有重叠,看起来应该海马/杏仁核和内侧颞叶,这些地方确实很容易有重叠。这个时候可能需要考虑选择保留皮层还是保留皮下结构,或者完全去除重叠部分。
- 假设选择保留皮下结构完整,去除皮层中与皮下结构重叠的部分,可以采用如下代码试试:
fslmaths Schaefer.nii.gz -mul Tian.nii.gz -bin overlap_mask.nii.gz
fslmaths Schaefer.nii.gz -bin -sub overlap_mask.nii.gz Schaefer_mask.nii.gz
fslmaths Schaefer.nii.gz -mas Schaefer_mask.nii.gz Schaefer_clean.nii.gz
上面代码得到的Schaefer_clean.nii.gz就是去除重叠以后的Schaefer模板,再与Tian模板进行相加。其他情况是类似的做法,你应该能搞定。
1 个赞
非常感谢!问题完美解决啦!![]()