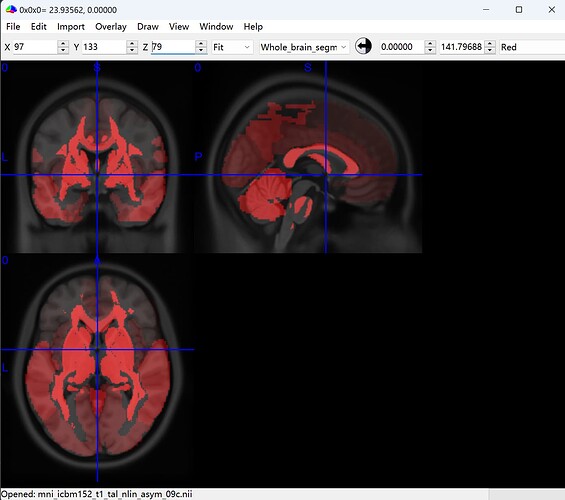
使用fMRIPrep预处理后的bold文件是在MNI152NLin2009cAsym空间,分辨率为3.5mm,大小为46x56x48。
使用 Longitudinal Atlas for Normative Human Brain Development and Aging over the Lifespan using Quantitative Susceptibility Mapping 中给出的QSM图谱,该图谱在MNI152空间,分辨率为1mm,大小为182x218x182。
我做了下面几个尝试:
-
使用flirt命令直接将QSM图谱配到预处理后得出的reference bold上:
flirt -in resampled_QSM_image.nii -ref sub-MNI0148_ses-01_task-rest_run-1_space-MNI152NLin2009cAsym_boldref.nii.gz -out resampled_QSM_image2.nii -applyxfm -usesqform -
先将QSM图谱重采样到3.5mm分辨率,大小为52x62x52,然后再将重采样后的图谱与reference bold进行配准。
但是上述两种方法都会遇到 配准后的QSM图谱中一些脑区缺失的问题。
我觉得可能是因为QSM图谱除了大脑外还包含皮下,小脑以及脑干区域,导致配准过程中脑区的缺失,请问老师怎么看这个问题,以及有没有解决方法呢?
谢谢老师能抽出时间解答我的问题!