投了一个相对容易接受的杂志,3个审稿专家,1拒绝,1小修,1大修。小修审稿专家,主要提出了一些语言性的问题。大修审稿专家说阴性结果也很重要,需要在表格和图片中补充阴性结果。我利用GBSS分析2组间,每个MRI参数中,都只有1个差异clusters,表格就相对简单,部分表格结构如下。
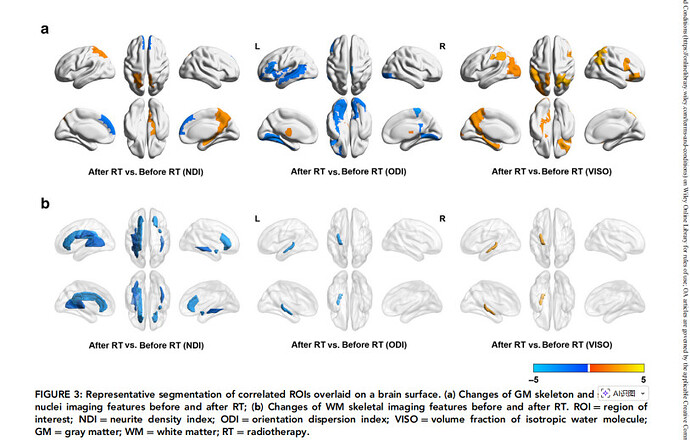
图片类似于这篇文章中的这样的图。可视化是利用brainnet viewer
审稿专家意见如下 2.In addition, Tables 2 and 3 are overly simplistic and do not adequately present important negative findings.
6.Figures 2 and 3 supplement important negative results.
困惑的点是:1.我所用那个GBSS方法得出来的就只有差异的结果,没有差异的脑区不能直接得到。我想用dpabi软件,然后用AAL或者其他模板对所有脑区提值再比较,这样可不可行呢,2.如果可行,有没有必要呢?因此,比较没有差异的脑区和纤维束的有很多个(AAL脑区大脑应该是90个),全都都展示出来的话,表格太大,没啥有用的信息,再就是在图片中,如何展示阴性结果呢,感觉很费解。
此外,这个专家还有一个疑问是:Please specify the source of the software schematic and add appropriate attribution in the figure legend, if applicable.
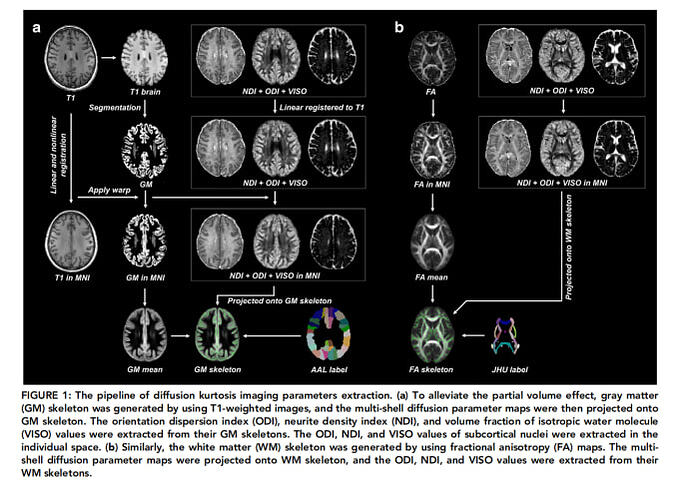
我没弄清楚这个问题是针对前面结果可视化的图,还是针对我做的图像后处理流程图的问题?
图像后处理流程图 类似于下面这个
请老师不吝赐教。