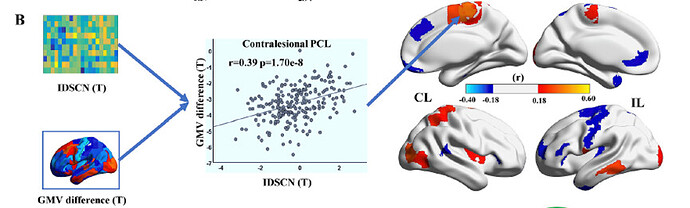
我参考一篇文献做个体化结构协变网络的分析,但是关于IDSCN与局部灰质体积的空间相关性分析部分不是很懂,请教一下各位。在这篇论文中,作者构建了每个患者的IDSCN,通过NBS识别平均异常IDSCN连边,使用两独立样本t检验比较病例组和对照组的灰质体积差异(我猜应该是ROI水平的分析),然后采用Spearman相关性来分析异常IDSCN连边和局部灰质体积差异的相关性,就是这最后一部分我不太清楚,能否给我解答一下是如何实现的?以下是部分图表和论文正文描述。论文:Zhang, H., Guo, J., Liu, J., Wang, C., Ding, H., Han, T., Cheng, J., Yu, C., & Qin, W. (2025). Reorganization of cortical individualized differential structural covariance network is associated with regional morphometric changes in chronic subcortical stroke. NeuroImage. Clinical, 45, 103735.
- 我猜测是图B中的矩阵的每一行与GMV difference进行相关,矩阵的每一行表示某个脑区与其他脑区的结构共变的组间差异(用T值表示),GMV difference是每个脑区的GMV的组间差异(用T值表示),所以这个相关反映的应该是结构共变的组间差异与GMV的组间差异的关联。
- 不过做空间相关需要考虑自相关性,否则显著性是严重高估的,因为脑区之间不是独立的,违背了一般相关分析的假设,需要使用诸如spin test这样的方法来进行假设检验。更详细的讨论可以参考这篇文献: Markello, R. D., & Misic, B. (2021). Comparing spatial null models for brain maps. NeuroImage, 236, 118052. https://doi.org/10.1016/j.neuroimage.2021.118052
好的,明白了,谢谢老师。我还想问另一个问题:我用cat12处理了所有被试的T1结构像,基于DK40脑图谱提取了所有受试者全脑68个脑区的平均皮层厚度,导出到excel里,对每个脑区的皮层厚度进行了组间比较并校正p值,如何把分析后的显著结果放回到DK40脑图谱上展示呢?(我知道cat12里有ROI analysis,我这里导出到excel分析是因为我对部分患者做了翻转操作,对右侧病变的患者,将皮层厚度数据改到对侧,使所有的病灶侧在左侧,病灶对侧为右侧,然后再分析)
可以参考这个帖子来进行可视化,基本思路就是把每个脑区的数值放回图像文件中,然后对图像进行可视化。
非常感谢!