Tgin
1
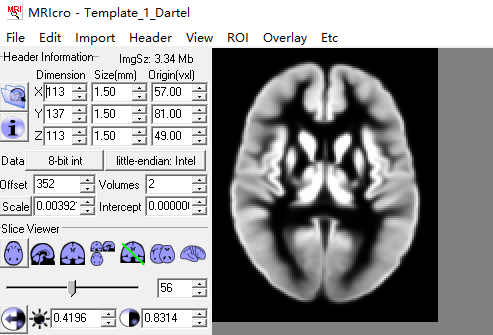
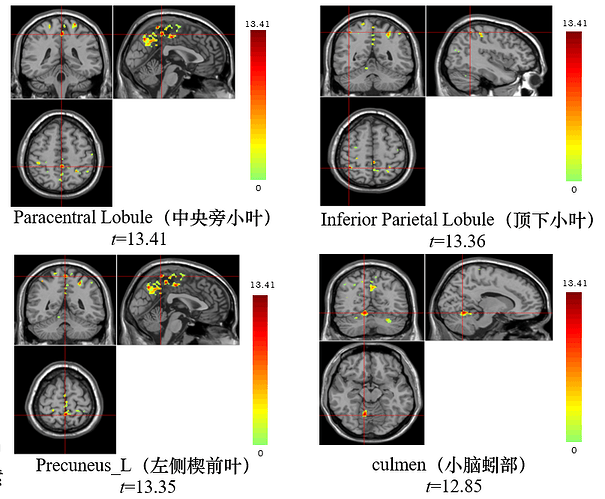
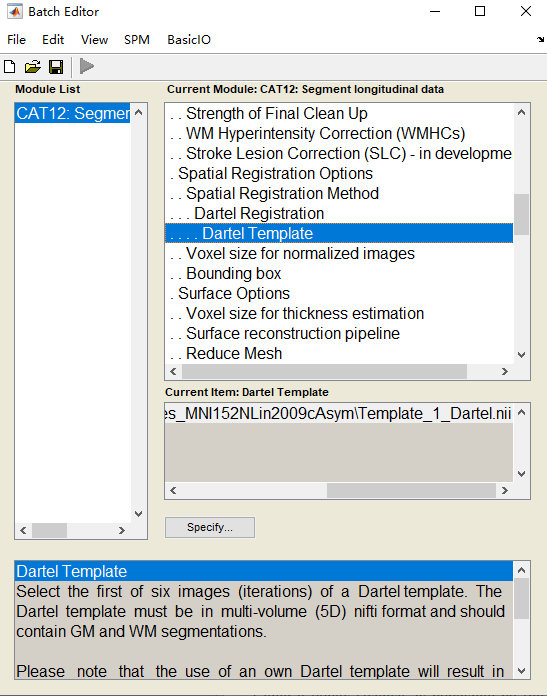
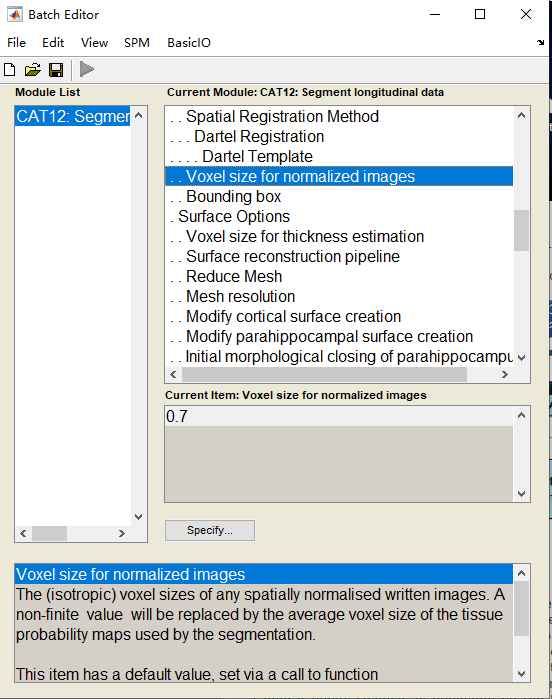
我用spm12下的工具cat12进行7T结构像的VBM分析,我一共有17个被试,每个被试包含两个时间点,我想纵向比较这两个时间点的灰质体积变化,所以做了配对t检验,映射模版为ch2,但检验激活结果有些跑到白质上去了,目前不知道问题出在哪。第二张图是时间点1>时间点2的激活结构,后三张是cat12里面的参数设置,因为我的数据分辨率是0.7mm,所以在voxel size那里改成了0.7,配准方法用的dartel,模版路径为:D:\MATLAB\spm12\toolbox\cat12\templates_MNI152NLin2009cAsym\Template_1_Dartel.nii
目前考虑可能是ch2模版的问题,但换了MNI152模版(0.74mm)依然偏离,因此我想找一个专用于7T的映射模版但没有找到,现在怀疑可能是Template_1_Dartel.nii模版导致配准出现误差,但这个模版应该找什么替换掉呢,自己创建一个自己被试的dartel模版可不可行呢
Tgin
3
老师您说的第二种解决方式,计算被试的平均灰质图应该是在被试的个体空间吧,这样我要想找某激活点坐标对应的脑区应该怎么找呢,还是说用这些被试创建一个dartel模版然后再配到MNI空间,然后把激活结果映射到这个标准的dartel模版上吗
Tgin
4
我还有几个问题想要请教一下老师:1.cat12里面有shooting和dartel两种配准方法,这两种方法哪一个更好呢,我看cat12手册里说shooting是dartel的改进版 2.我的MRI数据是7T的,分辨率比较高,cat12在分割的时候是根据TPM模版来的吗,如果是的话这种高分辨率的优势可以在分割中体现出来吗 3.在voxel size这里改成0.7mm是不是没有意义,因为这里的配置模版都是1.5mm的,改成0.7mm仅仅是上采样,原始的高分辨率信息已经没有了
Alex
5
所有被试只有都位于相同的空间(也就是MNI空间)才能平均,所以平均的灰质图是位于MNI空间的。
Alex
7
另外,我注意到你似乎认为,图像转换的过程是先从个体的0.7mm重采样到模板的1.5mm,然后再重采样到0.7mm。实际上转换是直接从个体的0.7mm采样到模板空间的0.7mm,尽管变形场是根据1.5mm的模板估计的。